[Quipu Issue Paper] Bioinformatics Knowledge Management Ⅰ - Next Generation Bioinformatics
- Posted at 2010/03/29 17:30
- Filed under 생물정보
연재 순서
1. Assembly
2. Variation study
3. Expression study
4. Epigenomics
5. Genome Annotation
6. Next Generation Bioinformatics
7. Data Management for web 2.0 Era
8. Semantic Network for Integrated Biology Data
9. Gene Network Discovery by Text-mining
10. Centralization for High-throughput Data Analysis
이번 연재에서는 NGS Application의 마지막 내용으로 Next Generation Sequencing 데이터를 분석하고 처리하기 위해서 이에 적합한 새로운 형태의 생물정보학인 'Next Generation Bioinformatics'에 대해 알아보겠습니다.
3-1. Next Generation Bioinformatics
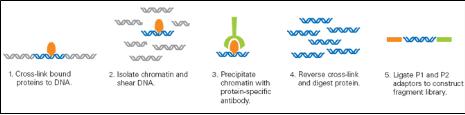
Applied Biosystems, Illumina 그리고 Roche 등과 같은 분석장비 개발회사에서 출시한 Next Generation Sequencers의 출현으로 전통적인 유전체 데이터 분석법에 새로운 변화와 도전이 요구되고 있다. 이러한 Sequencer들은 전에는 생각할 수 없었던 많은 양의 시퀀스 데이터를 쏟아내고 있고 이것은 생물정보학과 전산 생물학에 다양한 변화와 혁신을 초래하였다.
Next Generation Sequencing 데이터를 분석하고 처리하기 위해서 이에 적합한 새로운 형태의 생물정보학, 즉 ‘Next Generation Bioinformatics’에 대한 준비를 해야 할 것이다. NGS 데이터를 다룰 수 있는 충분한 저장장치, 관리 솔루션 그리고 생물정보학 분석 파이프라인 구축이 성공적인 NGS 연구에 필수적인 요소이다.
현재 대다수의 생물정보학 전문가들은 생물학자들이 다루기 힘든 커맨드 라인 방식의 데이터 처리로 실험 연구자들과의 분석 결과 검토를 위한 자료를 따로 작성하고 있다. 이는 생물학 데이터가 NGS의 도입에 의해 폭발적으로 증가된 상황에서는 매우 소모적인 것으로 실험 연구자들이 쉽게 분석결과를 검토하고 판별할 수 있는 플랫폼 개발이 요구되며, 직관적이거나 그래픽 사용자 인터페이스에 대한 요구를 좀 더 다양하게 충족시켜야 함을 나타낸다. 뿐만 아니라 대부분의 초기 분석이 리눅스와 같은 유닉스 환경에서 이뤄지고 있고, 생물학적 의미론을 분석하는 단계에서는 대부분 실험 연구자들이 이용하는 윈도우 환경에서 이뤄지므로 이들 간의 유기적인 데이터 교류를 위한 포맷 변화도 필요한 실정이다. 따라서 운영체제에 상관없이 NGS 데이터를 분석할 수 있으며, 서로 다른 운영체제에서도 데이터를 자유롭게 입출력을 할 수 있는 시스템 마련이 필요하다. 또한 공동 연구 및 컨소시엄을 통한 분석 방법이 늘어나는 추세이므로, 분석 데이터를 공동으로 관리할 수 있는 데이터베이스의 구성, 분석 프로그램의 표준화 및 정규화 그리고 많은 프로그램들을 연계한 효율적인 데이터 분석 파이프라인 구축 또한 요구된다.
앞으로 NGS 데이터는 임상 진단과 개인 맞춤 의약 연구에 직접적으로 이용되어질 전망이다. 이에 앞서 언급된 차세대 생물정보학에 대한 다양한 요구들이 쏟아질 것이다. 이러한 문제들이 해결되지 않는다면 조만간 생물정보학이 생물학 관련 연구에 큰 걸림돌이 될 수 있을 것이다[1].
다음 연재에서는 웹 2.0 시대에 맞추어 다양한 분야에서 생산된 데이터를 효율적으로 관리하는 방법에 대해 알아보겠습니다. 많은 관심 부탁드립니다.
참고문헌
1. Kwok-Wing Stephen Tsui (2009) Next Generation DNA Sequencing and Bioinformatics: Bottlenecks and Opportunities. The Third International Symposium on Optimization and Systems Biology
Posted by 人Co
- Tag
- Applied Biosystems, Bioinformatics, Illumina, insilicogen, NGS, Roche, Sequencer, 웹 2.0, 인실리코젠
- Response
- No Trackback , No Comment
- RSS :
- https://post-blog.insilicogen.com/blog/rss/response/64